| 高质量基因捕获测序如何实现? | 您所在的位置:网站首页 › 基因捕获技术原理知乎 › 高质量基因捕获测序如何实现? |
高质量基因捕获测序如何实现?
|
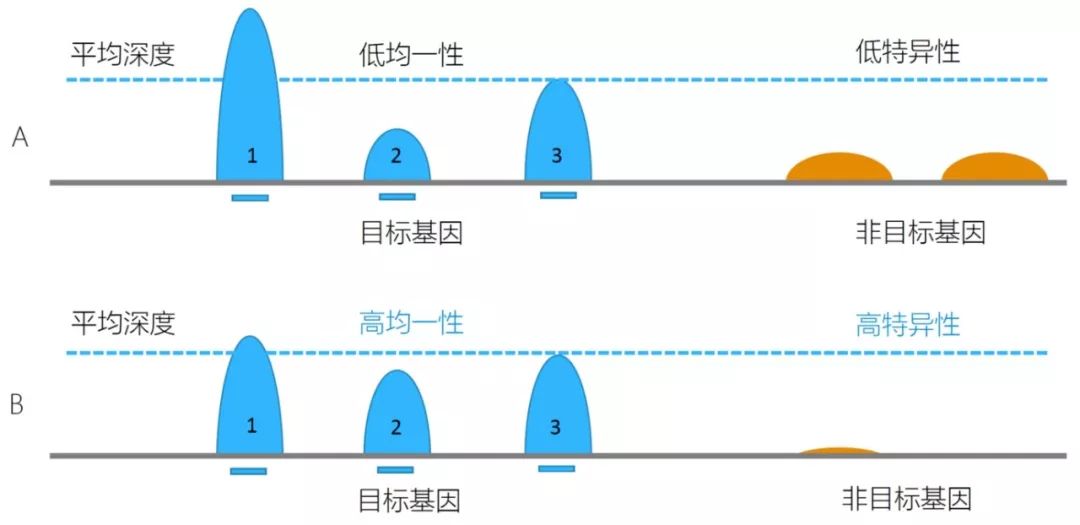
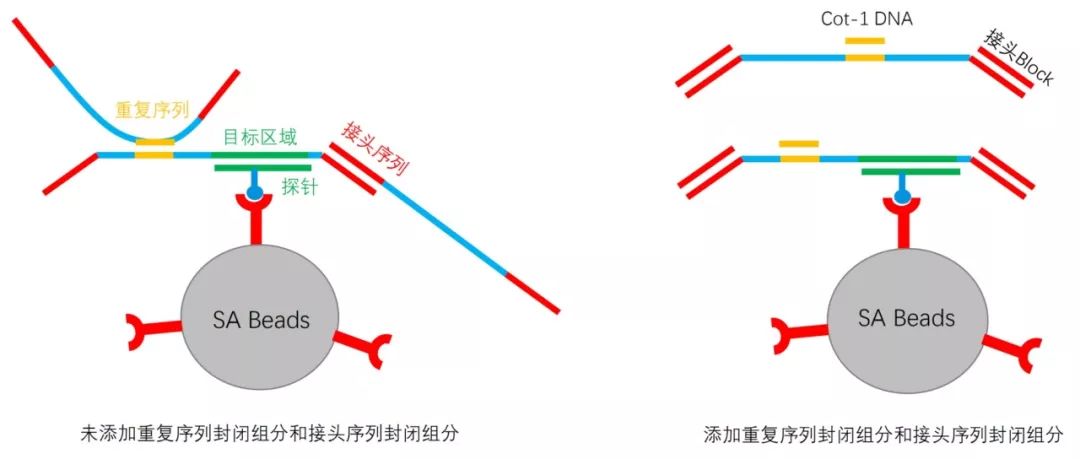
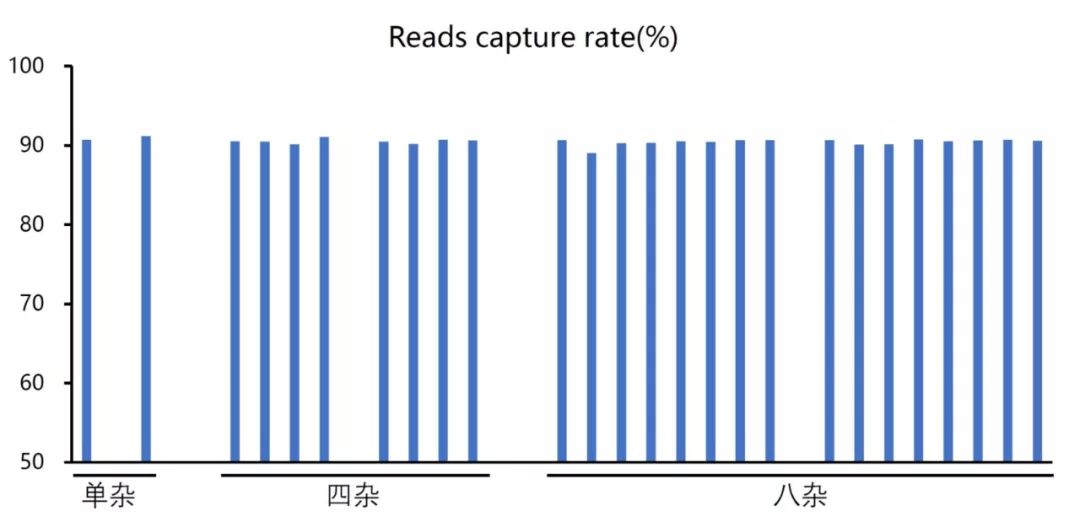
近十几年来,NGS(二代测序技术)的快速发展使得DNA测序成本大幅降低,然而就现阶段而言,全基因组重测序的成本依然很高,且得到的海量数据分析速度缓慢,无法大规模地应用。靶向测序技术可以将感兴趣的基因组区域富集出来测序,单个样本测序数据产出少且分析速度较快,因此更能经济高效地发挥NGS技术的优势,广泛应用到临床检测、健康筛查等众多领域。另外,靶向测序可以对目标区域进行深度测序,增加了目标区域内遗传变异的检测灵敏度和准确性。在技术原理上,靶向测序的方法主要分为两种:杂交捕获测序和多重扩增子测序。多重扩增子测序即针对感兴趣的目标区域,设计多重PCR引物进行扩增富集并进行测序的技术。通常适用于检测几十到几千个位点,或几十kb以下的区域。杂交捕获测序,目前应用的主要是液相杂交捕获测序,即基于碱基互补配对原理,设计合成核酸探针,对DNA文库进行基于液相环境的目标区域杂交富集,并进行测序。液相杂交捕获测序可适用于几kb到上百Mb的基因组目标区域的检测,可检测SNV,InDel,CNV,SV,基因融合等变异。对于液相杂交捕获测序,会涉及到探针序列设计,探针合成,液相杂交捕获等多个技术卡点,整个实验过程较为复杂,从商业化公司定制试剂盒成为主流的选择。目前已有数家公司提供探针个性化定制服务,即基于客户提供的感兴趣的基因组目标区域,设计合成捕获探针,交付液相杂交捕获个性化定制试剂盒,国内有艾吉泰康等,国外有Agilent,Nimblegen,IDT等。那么,如何评估液相杂交捕获测序的数据质量,以及如何实现高质量的捕获测序呢? 目标区域捕获测序的数据质量主要通过以下数据指标来评价:目标区域覆盖度、捕获特异性、目标区域覆盖均一性等。目标区域覆盖度是很容易理解的,就是对于想要检测的目标区域,能够被测到的比例是多少,或者反过来说遗漏掉了多少。最理想情况是感兴趣的目标区域都能被覆盖到,但是由于探针设计时会考虑各种因素,如GC含量、序列的特征、序列的拷贝数等。由于有些区域的探针会影响到整个panel的效果,为了保证整体的基因捕获效果,会选择放弃这一小部分区域的捕获,这个比例大约是0.1-3%。目标区域捕获是基于碱基互补配对原则的,会允许一些碱基的错配,因此在捕获富集感兴趣的目标区域的同时,探针也会结合一些序列相似的非目标区域。在做目标区域捕获测序时,因为落在目标区域内的数据对于检测才是有意义的,因此我们会期望测序数据更多地落在目标区域,更少的落在非目标区域。落在目标区域的数据占总数据的比例,就是捕获特异性,即捕获效率。捕获效率高,就意味着测序数据的利用率高。如图1所展现的,B数据捕获特异性是高于A数据的。
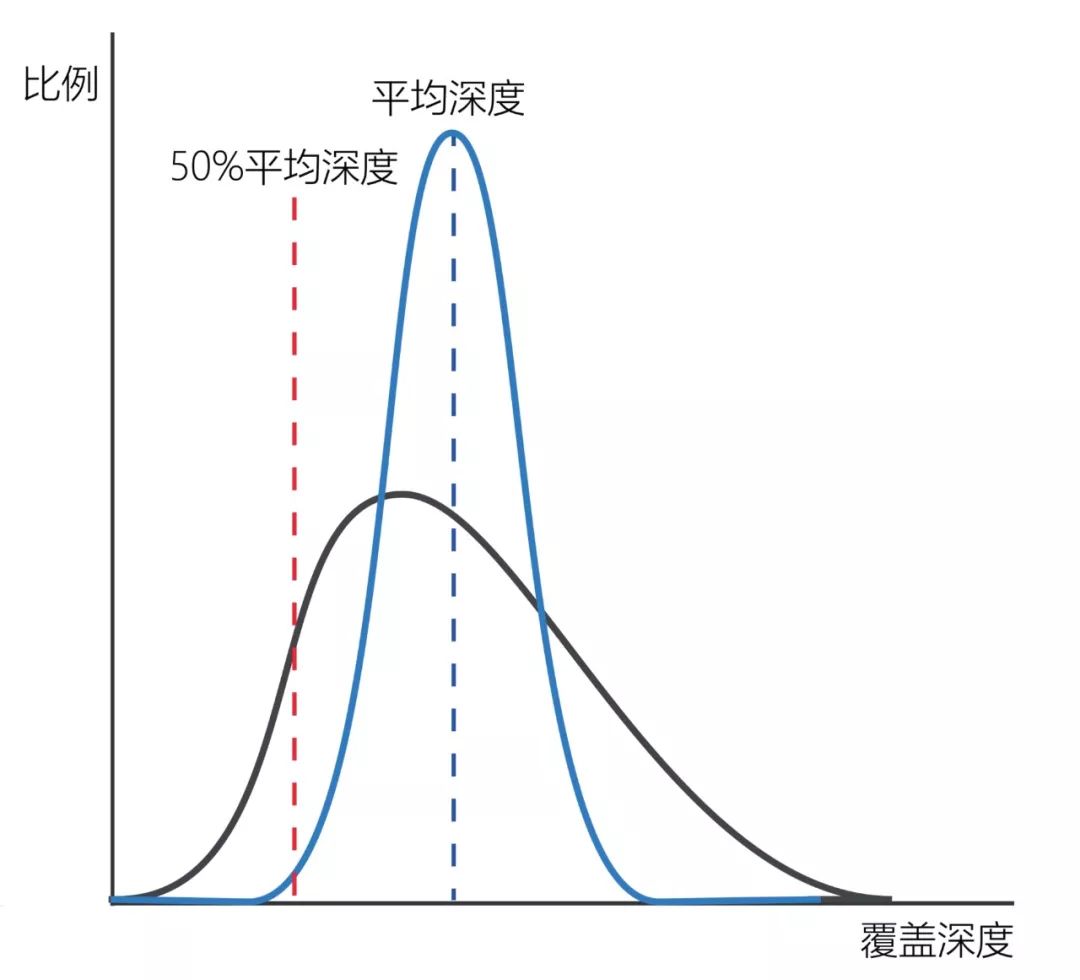
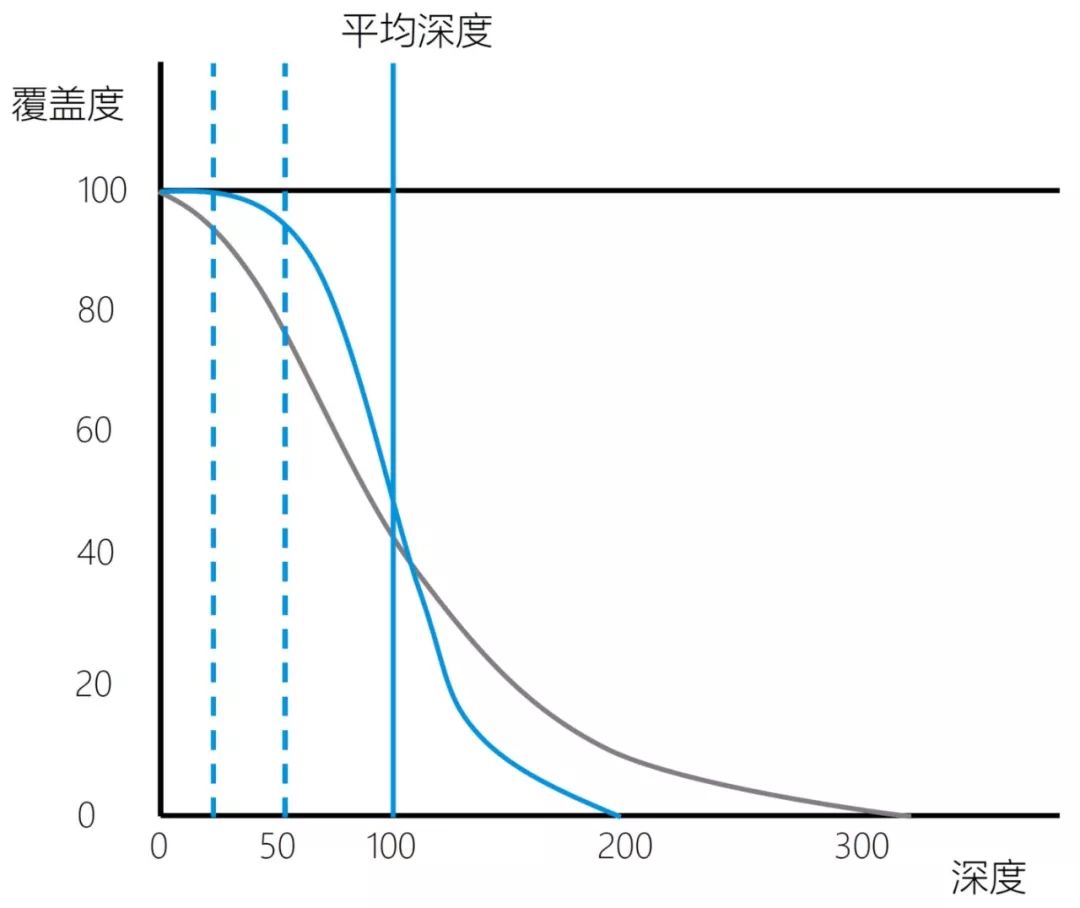
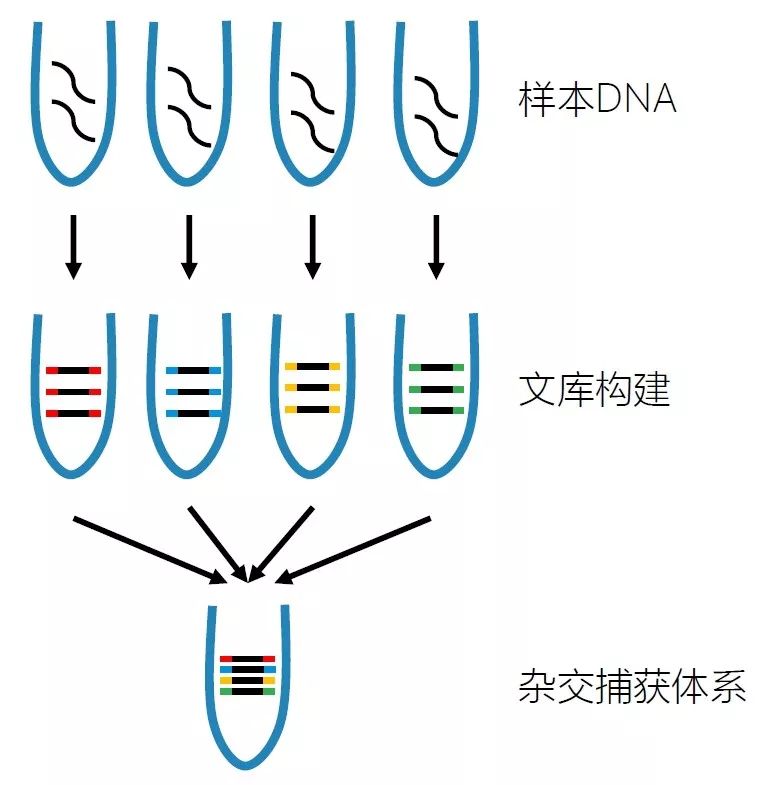
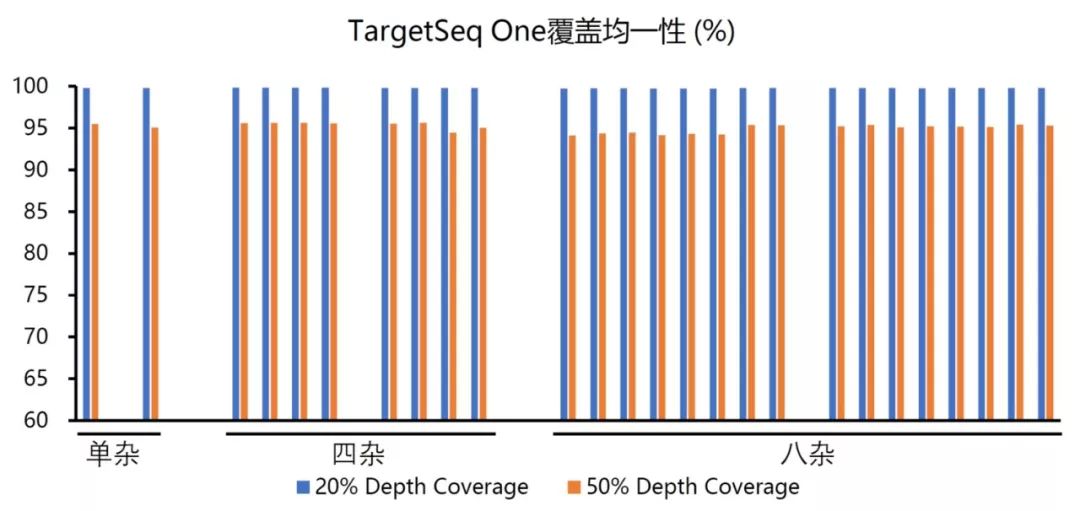
图4 位点测序深度累积分布图 那么覆盖均一性高意义在哪儿呢?覆盖均一性高,可以节省测序数据。举例来说,如果我们做的是遗传病的遗传变异检测,那么可能会要求测序数据对于目标区域的20X覆盖度达到98%,即98%的目标区域能够测20X以上的深度。如果测序数据的20%平均深度的覆盖度是98%,那么我们需要把目标区域平均深度测到100X。那么如果测序数据覆盖均一性有了较大的提升,20%平均深度的覆盖度达到了99%以上, 40%平均深度的覆盖度就达到了98%,那么我们在目标区域平均深度为50X的时候就可以达到目标区域的20X覆盖度达到98%的目标了,这样就可以节省50%的测序数据。如何实现对目标区域高度均一的覆盖呢?首先是文库的均一性,文库构建时,采用无序列偏差的DNA片段化方法,以及采用GC含量偏好性低的扩增酶,控制PCR扩增的循环数,有助于得到均一性较好的文库。由于不同序列的探针结合目标DNA片段的效率是不同的,在探针设计时需要预测探针的结合能力,并在探针合成时合理调整探针的比例,对结合能力弱的探针进行补偿。为了对目标区域进行高均一性覆盖,需要采用高度优化的杂交缓冲液和杂交实验流程进行捕获实验。卓越的技术指标是捕获测序技术的应用前提,而实验操作的简捷性则是靶向捕获技术广泛应用的必要保障,也是实验人员普遍关心的。简捷的实验操作可以大幅降低实验人员的工作量,节省实际动手操作的时间。将多管试剂在PCR仪上移液混合操作简化成单管实验操作,可以极大地简化实验操作,实验人员操作起来也更加从容。另外,多个文库混合在一个反应里进行杂交捕获,可有效降低实验成本,大幅提升实验操作效率(图5)。
图7 TargetSeq One覆盖均一性 互联网 喜欢作者 我要约稿 上一篇 | 下一篇 |
【本文地址】
公司简介
联系我们