| 研究 SNP 基因分型有哪些方法? | 您所在的位置:网站首页 › snp频率在哪里找 › 研究 SNP 基因分型有哪些方法? |
研究 SNP 基因分型有哪些方法?
|
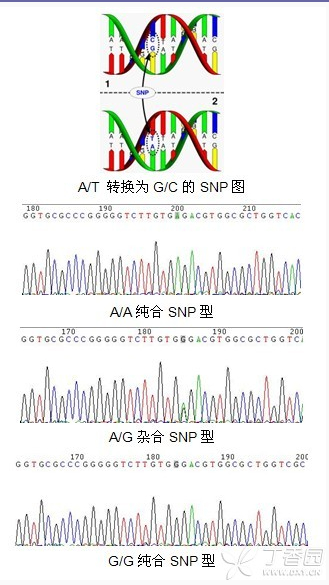
SNP,全称 Single Nucleotide Polymorphisms,是指在基因组上单个核苷酸的变异,包括转换、颠换、缺失和插入,形成的遗传标记,其数量很多,多态性丰富。从理论上来看每一个 SNP 位点都可以有 4 种不同的变异形式, 但实际上发生的只有两种, 即转换和颠换, 二者之比为 2:1。SNP 在 CG 序列上出现最为频繁, 而且多是 C 转换为 T , 原因是 CG 中的胞嘧啶常被甲基化, 而后自发地脱氨成为胸腺嘧啶。 一般而言,SNP 是指变异频率大于 1 % 的单核苷酸变异。在人类基因组中大概每 1000 个碱基就有一个 SNP , 人类基因组上的 SNP 总量大概是 3 ×10^6 个 。因此,SNP 成为第三代遗传标志, 人体许多表型差异、对药物或疾病的易感性等等都可能与 SNP 有关。 SNP 根据其在基因中的位置,可以分为基因编码区、基因非编码区、基因间隔区(基因之间的区域)。由于基因序列的兼并性,编码序列中的 SNP 不一定会改变蛋白的氨基酸序列。编码区的 SNP 有两种类型: 同义和非同义。同义单核苷酸多态性并不影响蛋白质序列,而非同义的则会改变蛋白质的氨基酸序列。 而不在蛋白质编码区的 SNP 仍可能影响基因剪接、转录子结合、信使 RNA 降解或非编码区的 RNA 序列。受到这种单核苷酸多态性(SNP)影响的基因表达被称为单核苷酸多态性表达(ESNP),可能发生在此基因的上游或下游。 直接测序法 目前很多朋友在研究 SNP 位点的时候,仍然在选用直接测序法,Sanger 测序原理为双脱氧终止法,会忠实的延伸出模板链上的碱基序列,在毛细管电泳中会依次收集各个碱基的荧光信号,SNP 则会在测序结果中出现如下套峰的情况,示例如下:
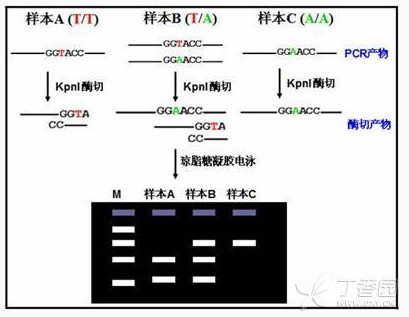
图片来源:Google 优点:直接测序法是目前最直观,准确性相对而言最高的 SNP 分型方法,适用于发现未知 SNP 位点,检测少量样本,少量位点的碱基多态性。 缺点:通量太低,且成本较高,但是随着现在高通量的测序技术的飞速发展,目的片段甚至全基因组的高通量测序也让直接测序法重新焕发活力! 片段长度多态性法 RFLP(Restriction Fragment Length Polymorphism,限制性片段长度多态性)是一种较早的进行 SNP 分型的技术,简单来说就是在包含 SNP 位点的序列中存在有特定的限制性内切酶酶切位点,而 SNP 位点基因型的改变则会使该酶切位点失效,这样根据酶切之后 PCR 片段长度的多态性即可得知对应的基因型,下面用一张图片来示意该方法的实验流程:
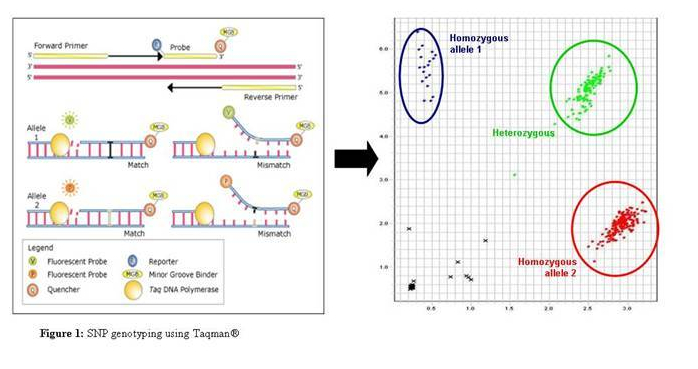
如上图所示,三种基因型的结果条带数目不一致,可以比较容易判读样本的基因型。 优点:适合小批量样本的分型实验,不需要特殊的仪器,只需要一台 PCR 仪以及电泳仪器即可; 缺点:通量小且对于位点要求高(需要特定的酶切位点),且没法儿准确的鉴别假阳性的情况(酶切不完全)。 针对上述情况,如果是没找到合适的酶切位点,或者说存在的酶切位点所需要的内切酶成本较高,可以通过在 PCR 引物上引入错配,得到理想的酶切位点; 其次,为了增大该种方法的检测精确性,一种方法是在 PCR 产物中选择一个内参酶切位点(与目标酶切位点一致,用以检测酶切是否完全),第二种方法就是改进出了荧光酶切方法,即在 PCR 的产物上添加上荧光,通过测序仪收集荧光信号,报告产物的长度,该种方法的优势在于毛细管电泳的精确性更高,分辨率更大,同时可以混合上样,降低实验分型的成本,提高效率。 飞行质谱法 基质辅助激光解吸电离飞行时间质谱(Matrix Assisted Laser Desorption/Ionization Time of Flight Mass Spectrometry,MALDI-TOF MS)技术的 SNP 分型原理是:先通过 PCR 扩增目标序列,然后加入 SNP 序列特异延伸引物,在 SNP 位点上延伸 1 个碱基。将制备的样品分析物与芯片基质共结晶,将该晶体放入质谱仪的真空管, 而后用瞬时纳秒(10 - 9s)强激光激发,基质分子吸收辐射能量,导致能量蓄积并迅速产热,使基质晶体升华,核酸分子就会解吸附并转变为亚稳态离子,产生的离子多为单电荷离子,这些单电荷离子在加速电场中获得相同的动能,进而在一非电场漂移区内按照其质荷比率的不同得以分离,在真空小管中飞行到达检测器。 MALDI 产生的离子常用飞行时间(Time-of-Flight,TOF)检测器来检测,离子质量越小,就越快到达。利用质谱分析对质量的灵敏度特别高的特点,很容易将仅含有一个不同碱基的两段基因序列区别开,推导出 SNP 分型。 优点:成本较低,不需要合成特殊的荧光引物,只需要一对 PCR 引物以及延伸引物即可;检测方便,灵敏度高,数据准确性有保证; 缺点:对于 SNP 位点两侧序列要求较高,存在特殊序列,如 SNP 位点,插入缺失等会影响准确性,另外,对于样本质量稍微有些高,补数据较为麻烦,如果样本质量不是很好的,建议谨慎选用;最后一点是检测成本低是基于位点数以及样本数较多的情况而言,目前市面上的公司一般是 25 - 30 个位点一个体系,384 孔板为一个反应收费。 Taqman 荧光探针法 Taqman 探针想必各位都不陌生,原理介绍如下: 该技术是由 ABI 研发的 SNP 分型技术,其技术原理如下:PCR 反应时,加入一对两端有不同荧光标记的 MGB 特异探针来识别不同等位基因(allele1 和 allele2),5’端为报告荧光基团(reporter),3’端为淬灭荧光基团 (quencher)。PCR 过程中,两个探针能与正向引物和反向引物之间的互补序列特异退火结合。当探针以完整形式存在时,由于能量共振转移,荧光基团只发出微弱荧光。 特异的探针与相应的等位基因结合后,DNA 聚合酶发挥 5’到 3’外切酶活性,把报告荧光基团切割下来,脱离 3’端淬灭荧光基团的淬灭作用(quench),从而发出荧光。两个探针的 5’端标有不同的荧光(FAM 或 VIC),3’端标有 MGB 淬灭基团结合体。根据检测到的不同荧光,可以判断相应样本的 SNP 等位基因型。
上图右侧即为 Taqman 实验分型后的结果图,以上,蓝色和红色代表两种纯合子,右上角的绿色则为杂合子,左下角的黑色为 NTC,其余地方散落的黑色的点则为由于样本原因无法准确分型的结果。 优点:操作简单,准确性高,判读也很方便,认可度高; 缺点:探针合成耗时较长,一般为 ABI 公司合成,从我自己的经历讲,国内合成的探针质量不稳定,价格偏高,通量小,一般为 1 - 2 个位点适用,对于样本的质量要求较高,除了样本无降解外,还需要浓度尽可能的一致,这样结果才会比较集中。 多重 SNaPshot 检测方法 SNaPshot 技术又称为小测序技术,是由美国应用生物公司 (ABI) 开发的主要针对中等通量 ( |
【本文地址】