| 超实用!微生物重测序分析软件 | 您所在的位置:网站首页 › bwa建立索引需要多久 › 超实用!微生物重测序分析软件 |
超实用!微生物重测序分析软件
|
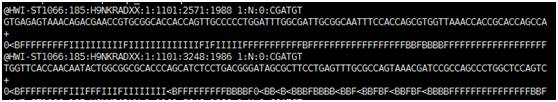
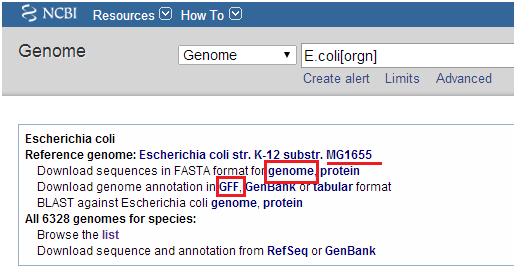
Fastq文件每四行表示一个read(如上图所示),其中第一第三行表示read名称等相关信息,第二行为read序列,第四行为第二行对应的每个碱基质量值。 参考基因组文件: NCBI下载的E.coli MG1655基因组序列ref.fa和基因组注释文件ref.gff(用于变异注释)
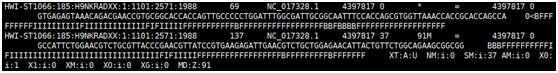
2. bwa mapping到参考基因组 1)为参考基因组建立索引 bwa index ref.fa #参数说明: -a BWT构建算法:bwtsw, is of rb2 [default],bwtsw适用于较长基因组,另外两个使用于短基因组; -p 索引的前缀[same as fasta name]; -b bwtsw算法模块长度,与-a bwtsw一起使用,[default 10000000]; 2)寻找SA coordinates bwa aln ref.fa sample.fq1.gz > sample.fq1.sai # pair-end bwa aln ref.fa sample.fq2.gz > sample.fq2.sai bwa sample ref.fa sample.fq1.sai sample.fq2.sai sample.fq1.gz sample.fq2.gz > sample.sam bwa aln ref.fa sample.fq.gz > sample.fq.sai # single-end bwa samse ref.fa sample.fq.sai sample.fq.gz > sample.sam sam文件格式如下,以@开头的行为注释行,没有@开头的部分为具体比对信息,每行表示一条read与参考基因组的比对情况,每行共有12列,依次为:read name,flag,参考序列编号,比对上的位置,mapping的质量值,简要比对信息表达式,下一个片段比对上的参考序列编号,下一片段比对到参考序列上的 第一个碱基位置,参考序列和比对上的序列共同组成的序列Template的长度,序列片段信息,序列质量值信息以及可选区域(格式为TAG TYPE VALUE)。
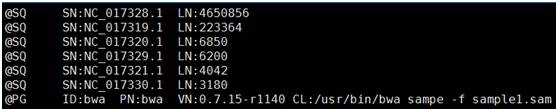
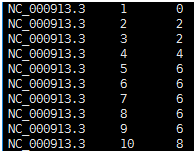
3)将sam进行排序,并转换为bam文件 samtools sort sample.sam –output-fmt BAM –o sample.sort.bam 参数说明: --output –fmt BAM 指定输出文件为bam格式文件; -o 输出文件名; 统计所有位点的测序深度 samtools depth –a sample.sort.bam > sample.depth 参数说明: -a 输出所有位点,包括深度为0的位点; -l read长度阈值,低于该长度的read将被忽略; -d 最大覆盖深度,默认8000; -q 碱基质量阈值; -Q 比对质量阈值; Sample.depth 文件(如下图所示)由三列组成,依次为染色体名,参考基因组位点,和该位点的覆盖深度。
Samtools 软件的安装和使用将在下期进行详细介绍。 三 参考文献 Li H, Durbin R. Fast and accurate short read alignment with Burrows-Wheeler transform.[J]. Bioinformatics, 2010, 25(14):1754-1760. doi: 10.1093/bioinformatics/btp324, pubmed:19451168. Ayat H, Doruk B, Toland A E, et al. Benchmarking short sequence mapping tools[J]. Bmc Bioinformatics, 2013, 14(1):184 供稿:协云基因微生物事业部 韩娜 想了解更多? 那就赶紧来关注我们 有问题请联系协和基因云 微信ID: geneworks返回搜狐,查看更多 |
【本文地址】