细菌或原核生物16S |
您所在的位置:网站首页 › 保守序列有哪些 › 细菌或原核生物16S |
细菌或原核生物16S
|
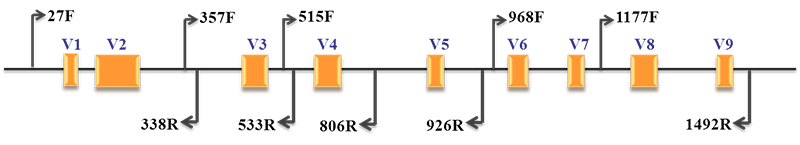
细菌核糖体RNA(rRNA)有三种类型:5S rRNA(120bp)、16S rRNA(约1540bp)和23S rRNA(约2900bp)。5S rRNA基因序列较短,包含的遗传信息较少,不适于细菌种类的分析鉴定;23S rRNA基因的序列太长,且其碱基的突变率较高,不适于鉴定亲缘关系较远的细菌种类;16S rRNA普遍存在于原核细胞中,且含量较高、拷贝数较多(占细菌RNA总量的80%以上),便于获取模板,功能同源性高,遗传信息量适中,适于作为细菌多样性分析的标准。 16S rRNA编码基因序列共有10个保守区和9个高可变区。其中,文献中常用的区域是V1-V2,V3-V4,V4-V5等区域。 细菌16S rRNA基因序列组成及引物选择 微基生物进行人体健康相关的研究与应用: 细菌16S rRNA 真核18S rRNA 古细菌16S 真菌ITS 功能基因 细菌或原核16S rRNA 真核生物18S rRNA 古细菌16S rRNA 真菌ITS 功能基因 微基生物提供与人体健康相关的生信/统计服务: 生物信息与统计学分析 物种组成图 (样品群落结构分析柱状图、多样品对比树图、样品群落结构分析柱状图) 微生物多样性分析/宏基因组 LEfSe差异分析 PCA差异分析 RDA环境因子分析等 更多微生态方向研究和生物信息方面服务,请详询:400-660-9270 细菌多样性分析的流程图如下: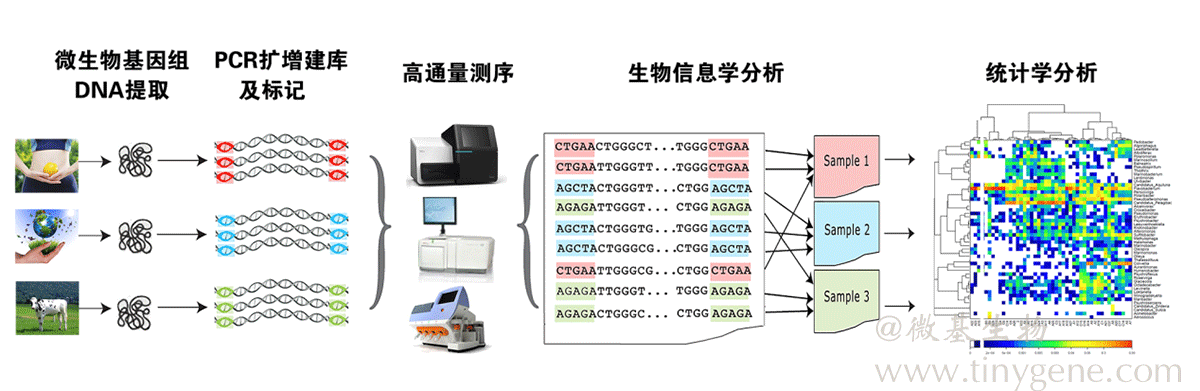 高通量测序分析流程
数据库:Silva,GreenGene,RDP 高通量测序分析流程
数据库:Silva,GreenGene,RDP
收集目前世界上最全面的三大微生物rRNA基因信息数据库。 高通量测序目前市面上常用的用于研究环境微生物的高通量测序平台有Illumina,BGI,PacBio和Thermo Ion。针对于细菌的16S rRNA基因序列分析,Illumina 测序平台凭借其测序读长长、测序周期短、通量大等特点,成为使用最为普遍的测序平台。 微基生物是国内首家采用Illumina MiSeq 2×300 bp平台进行微生物生态研究,其最大读长可达到550 bp,适合对V3、V4、V5区及V3-V4、V4-V5区进行测序分析。 生信/统计分析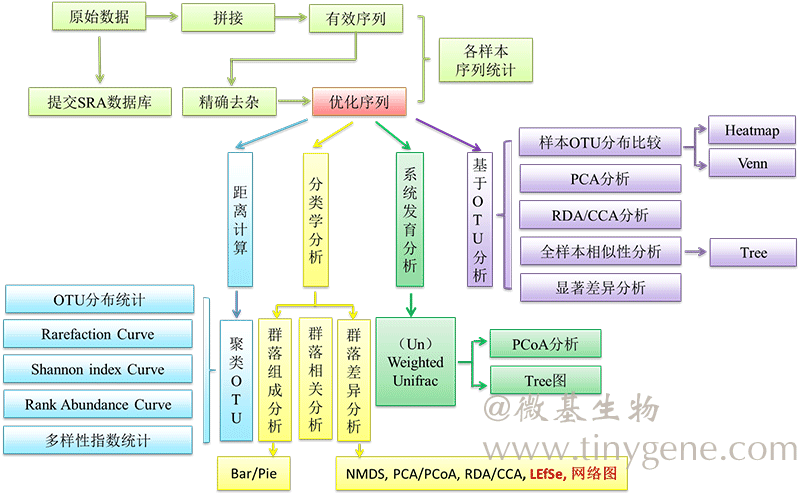 生信/统计分析流程 生信/统计分析流程
案例分析 标题:由长期的土壤移植引起的纬度和气候变化明显改变了土壤微生物的变化率
(2)由土壤移植引起的土壤微生物的变化 微生物随时间衰减的斜率可以用来衡量微生物群落的相似性。本研究中,在各个样本的微生物群落中都存在显著的的时间衰减关系。向北、向南移植的土壤中,微生物随时间衰减的斜率均比原位土壤的斜率大,尤其是在向南移植的土壤中。
随着温度的升高/降低,微生物的变化率也相应地增加。随着土壤向南移植,气候变暖,微生物群落的波动性增大,微生物群落的变化增加。向南移植对土壤微生物群落的变化具有出更好的效果。有趣的是,研究还发现细菌群落(门水平)的改变与分类学的分度有关。其中变形菌门、拟杆菌门和疣微菌门与门的丰度呈负相关,而酸杆菌门、放线菌门、后壁菌门和浮霉菌门与门的丰度呈正相关。
(3)细菌群落及系统进化树分析 在为期六年的试验中,三个样本共检测出78个OTUs,其OTU的数量非常少,分属于9个门。用MEGA 5作系统进化树,如下图所示。
其中,酸杆菌门中的Gp4和Gp6、节细菌属、硝化螺菌属、鞘氨醇单胞菌、Fervidicoccus、Sphingosinicella、Steroidobacter和Terrimonas是主要菌群。
(4)微生物演替与环境因子的关系
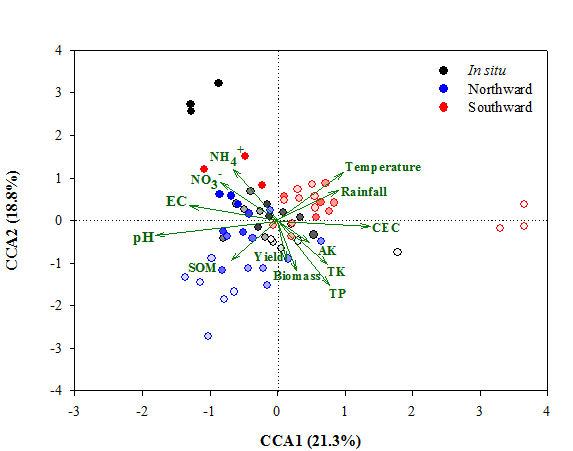
微生物的演替与环境因子之间的关系用CCA分析如下。结果表明,向北移植的土壤中,微生物群落的多样性与土壤的物理化学因子有关;而向南移植的土壤中,微生物群落的多样性受温度和降水的影响较大。 |
【本文地址】
今日新闻 |
点击排行 |
|
推荐新闻 |
图片新闻 |
|
专题文章 |
 研究领域:土壤微生物 分析物种:细菌 取样方法:从中科院封丘站取1.4*1.2*1.0体积的土壤,分别向北移植到黑龙江海伦站,向南移植到江西鹰潭站。每组设3个重复,于2006-2011年每年的8-9月取20 cm的表层土,密封在聚乙烯包装袋中,于-80︒C保存。 高通量测序平台:Illumina MiSeq 2×150 测序区域:16S rRNA gene V4区 样本数及分组:分3组,3个重复,共63个样本。 研究背景: 生物群体对由某些人为因素造成的潜在威胁(如气候改变)的响应是目前生态学研究的一个重要挑战。鉴于微生物在生物地球化学循环中的重要作用,它们对气候改变的响应有可能导致生态结构的改变。之前已有研究指出,温度是影响土壤微生物组成和生态功能(土壤的呼吸作用、有机物的含量、固氮水平)的重要因素。而不同地域之间的土壤移植为研究微生物群落对气候变化的响应提供了新的研究方法和思路。 [/tabs] 主要结果: (1)微生物的演替 随着时间的推移,向北、向南移植的土壤中,微生物的群落组成差异越来越大,微生物多样性逐渐增加。
研究领域:土壤微生物 分析物种:细菌 取样方法:从中科院封丘站取1.4*1.2*1.0体积的土壤,分别向北移植到黑龙江海伦站,向南移植到江西鹰潭站。每组设3个重复,于2006-2011年每年的8-9月取20 cm的表层土,密封在聚乙烯包装袋中,于-80︒C保存。 高通量测序平台:Illumina MiSeq 2×150 测序区域:16S rRNA gene V4区 样本数及分组:分3组,3个重复,共63个样本。 研究背景: 生物群体对由某些人为因素造成的潜在威胁(如气候改变)的响应是目前生态学研究的一个重要挑战。鉴于微生物在生物地球化学循环中的重要作用,它们对气候改变的响应有可能导致生态结构的改变。之前已有研究指出,温度是影响土壤微生物组成和生态功能(土壤的呼吸作用、有机物的含量、固氮水平)的重要因素。而不同地域之间的土壤移植为研究微生物群落对气候变化的响应提供了新的研究方法和思路。 [/tabs] 主要结果: (1)微生物的演替 随着时间的推移,向北、向南移植的土壤中,微生物的群落组成差异越来越大,微生物多样性逐渐增加。 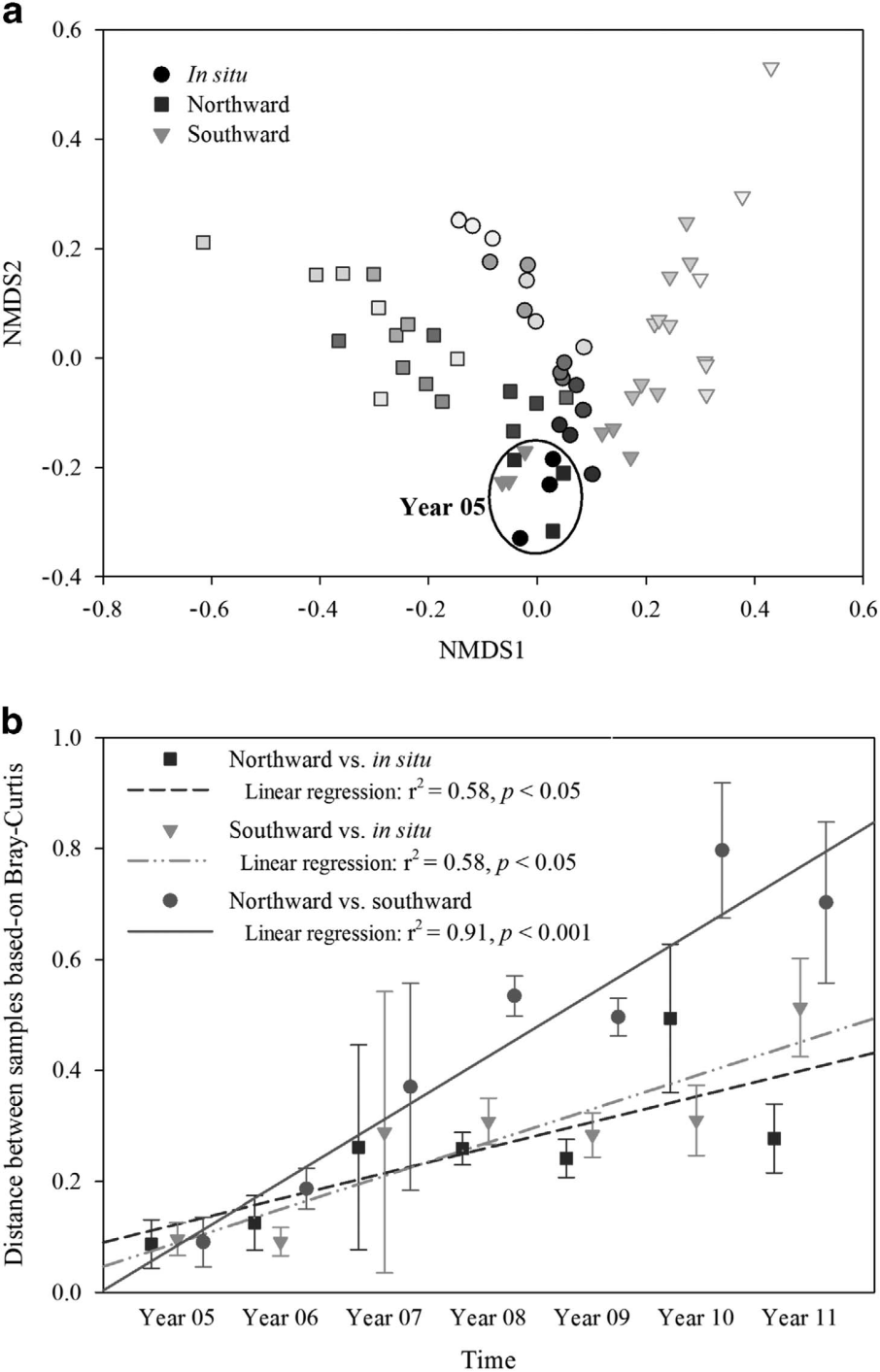
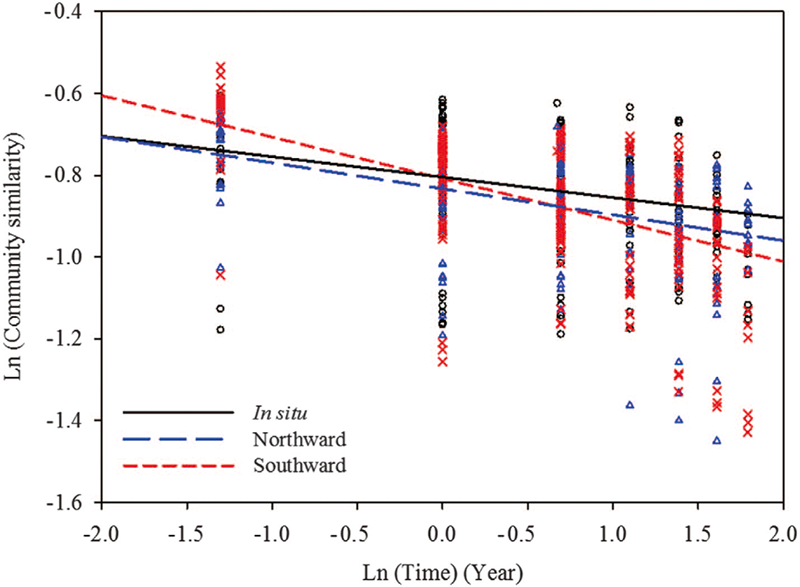
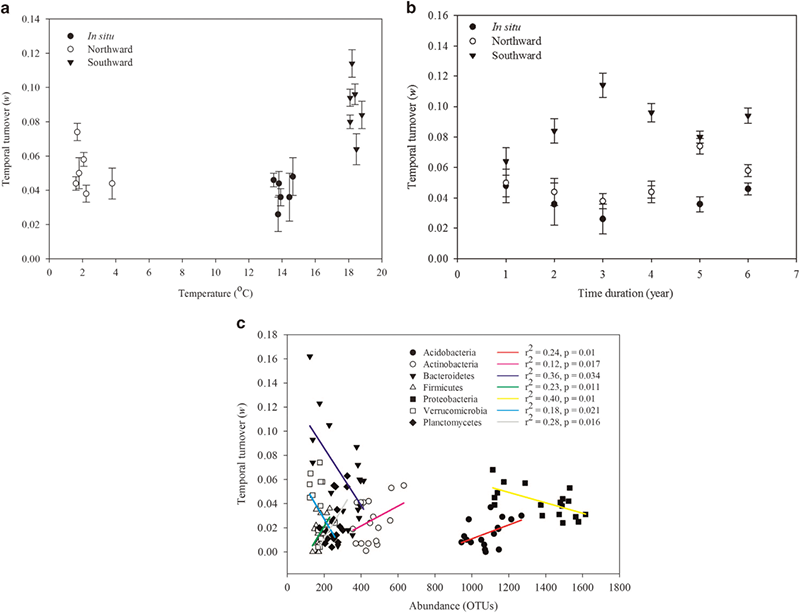
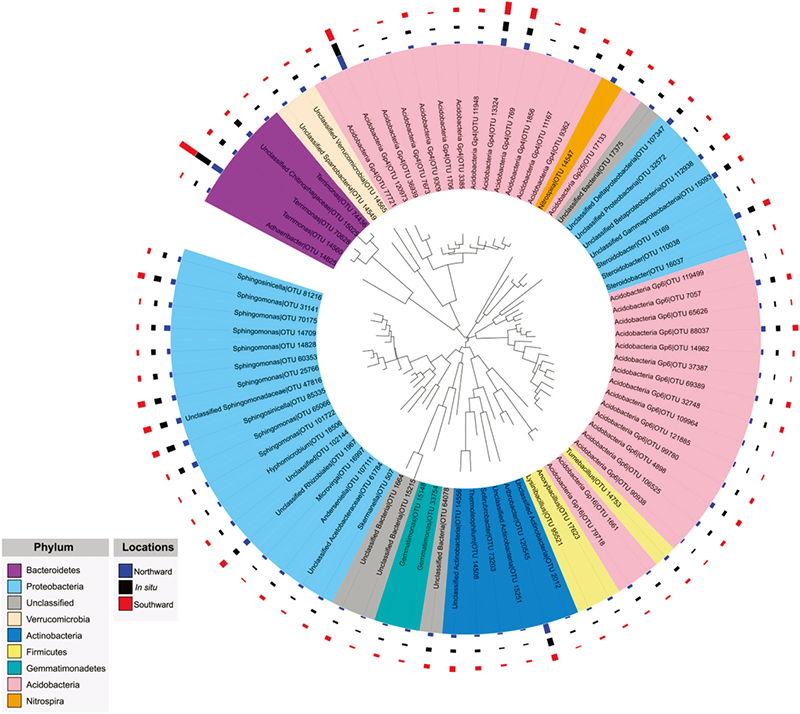
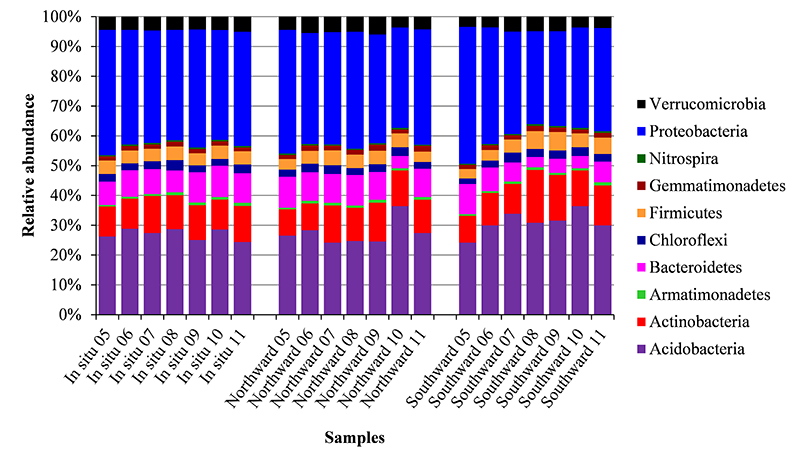
 本研究采用illumina MiSeq测序平台,对经过移植的土壤微生物为研究对象,扩增了细菌16S rRNA基因的V4区域,从而得到土壤中细菌种群分布的相关信息,对其中的微生物种群变化进行了调查研究。
此实验采用illumina MiSeq 2*150双端测序,每个样品可得到948,765条序列,其中有效序列为10,947条。研究发现,与原位土壤相比,向北移植(低温)的土壤中,细菌的丰度增加,演替速率升高;向南移植(高温)的土壤中,细菌的丰度降低,而演替速率达到最高,即稳定性不好。推断这是由于高温环境容易引起高的代谢率和更加激烈的生存竞争造成的。 原文链接:http://www.nature.com/ismej/journal/vaop/ncurrent/full/ismej201578a.html 参考文献: Liang, Y., Y. Jiang, F. Wang, C. Wen, Y. Deng, K. Xue, Y. Qin, Y. Yang, L. Wu, J. Zhou and B. Sun (2015). “Long-term soil transplant simulating climate change with latitude significantly alters microbial temporal turnover.” ISME J.
本研究采用illumina MiSeq测序平台,对经过移植的土壤微生物为研究对象,扩增了细菌16S rRNA基因的V4区域,从而得到土壤中细菌种群分布的相关信息,对其中的微生物种群变化进行了调查研究。
此实验采用illumina MiSeq 2*150双端测序,每个样品可得到948,765条序列,其中有效序列为10,947条。研究发现,与原位土壤相比,向北移植(低温)的土壤中,细菌的丰度增加,演替速率升高;向南移植(高温)的土壤中,细菌的丰度降低,而演替速率达到最高,即稳定性不好。推断这是由于高温环境容易引起高的代谢率和更加激烈的生存竞争造成的。 原文链接:http://www.nature.com/ismej/journal/vaop/ncurrent/full/ismej201578a.html 参考文献: Liang, Y., Y. Jiang, F. Wang, C. Wen, Y. Deng, K. Xue, Y. Qin, Y. Yang, L. Wu, J. Zhou and B. Sun (2015). “Long-term soil transplant simulating climate change with latitude significantly alters microbial temporal turnover.” ISME J.