| 如何下载NCBI上的10X单细胞测序原始数据并用于Cell Ranger分析 | 您所在的位置:网站首页 › 测序原始文件格式 › 如何下载NCBI上的10X单细胞测序原始数据并用于Cell Ranger分析 |
如何下载NCBI上的10X单细胞测序原始数据并用于Cell Ranger分析
|
1. 获取数据的SRR*
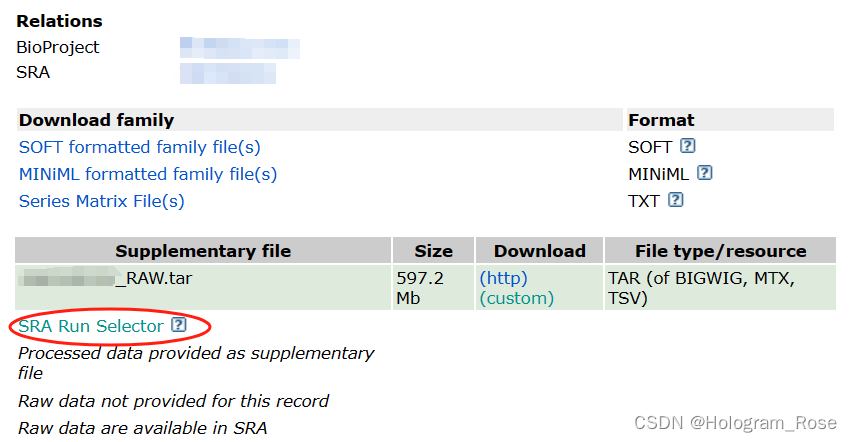
根据参考文献提供的GEO数据链接,直接在浏览器打开,或者NCBI官网检索GSE号,在数据网址的最下方点击SRA Run Selector链接跳转至新的页面,该页面包含原始fastq文件的SRR编号,和样本的一些基本信息。
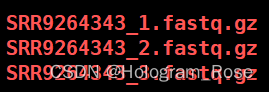
以SRR9264343为例 fastq-dump --split-files --gzip SRR9264343下载完成后有以下三个文件,Cell Ranger mkfastq处理之后,一般会产生3个fastq.gz文件,分别是I1文件,8bp的样本barcodes;R1文件16bp feature barcodes + 10 bp/12 bp UMI; R2文件转录组的reads文件。
从SRA Run Selector页面,单击单个样本的SRR*,可以跳转至以下页面并点击Data access,根据Original format处的信息,可以清晰地分辨下载后3个的文件分别对应的具体文件。
Cell Ranger 要求fastq文件的命名符合 bcl2fastq文件的命名规范,即以下模式: [Sample Name]_S1_L00[Lane Number]_[Read Type]_001.fastq.gz 修改文件名,使其符合规范。或者直接将上面original format信息中Name列文件名修拷贝过去,修改后的文件名如下:
参考网址 https://kb.10xgenomics.com/hc/en-us/articles/115003802691-How-do-I-prepare-Sequence-Read-Archive-SRA-data-from-NCBI-for-Cell-Ranger understand 10x scRNAseq and scATAC fastqs | DNA confesses Data speak |
【本文地址】
公司简介
联系我们