| 利用VCF文件构建系统发育树 | 您所在的位置:网站首页 › 构建系统发育树至少要多少个菌类 › 利用VCF文件构建系统发育树 |
利用VCF文件构建系统发育树
|
导读 本文将介绍三种使用VCF文件,构建系统发育树的方法,包括程序的安装,使用,已及系统发育树的可视化与美化。 1. VCF2DisVCF2Dis[1]是一种新的简单高效的软件,用于计算基于VCF格式的距离矩阵 1.1. 安装代码语言:javascript复制# 下载 wget -c https://github.com/hewm2008/VCF2Dis/archive/v1.47.tar.gz # 解压 tar -zxvf v1.47.tar.gz # 进入程序目录 cd VCF2Dis # 编译 make ; make clean # 测试运行 ./bin/VCF2Dis 1.2. 距离矩阵利用VCF2Dis生成距离矩阵代码语言:javascript复制VCF2Dis -i test.vcf -o test.mat 1.3. mat2nwk文件转换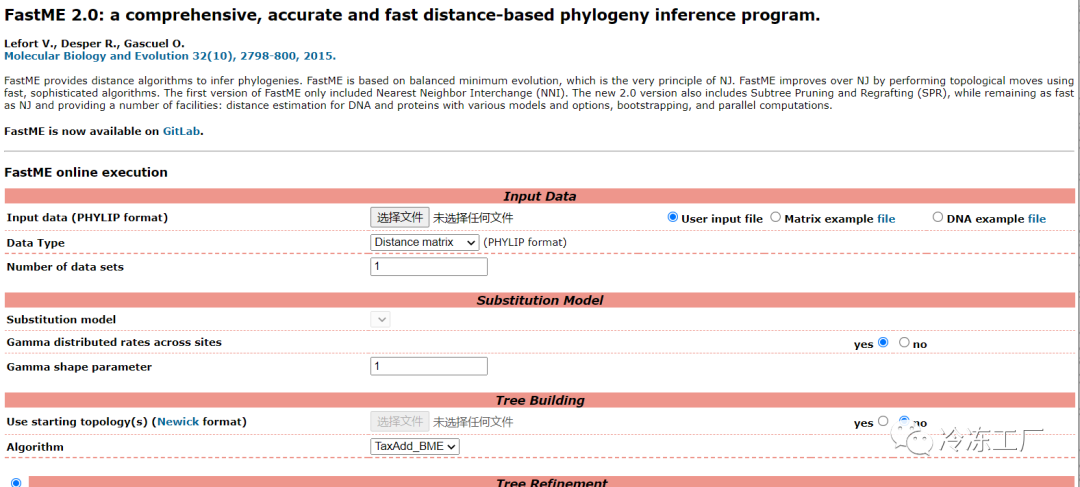 FastMe2.0 上传距离矩阵到在线网站, FastMe2.0[2]。上传以后,选择Data type为Distance matrix。然后根据自己的需要进行配置,最后填入任务名称和Email来获取结果通知。 结果下载点击下载结果 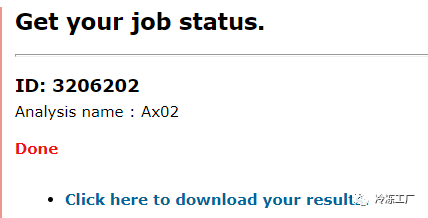 结果下载 结果文件是一个压缩文件,里面包含: 一个.nwk文件用于进化树可视化 结果文件 stats.txt记录了文件转换过程中,选择的参数 stdout.txt转换过程中的日志文件,记录了程序的运行过程 1.4. iTOL美化十分推荐利用iTOL对进化树进行美化,该程序是网页版,配置简单,结果十分漂亮。 导入iTOL[3]美化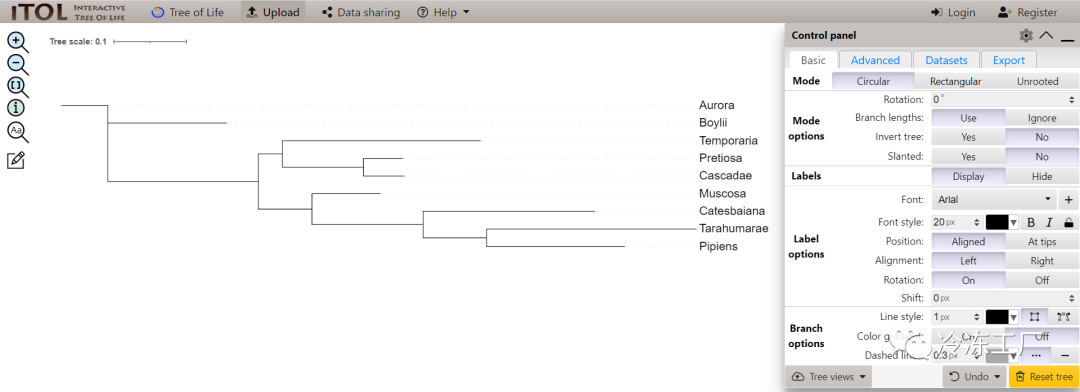 iTOL 2. PhylipPHYLIP[4]是用于推断系统发育的免费程序包。 2.1. 安装源码编译安装代码语言:javascript复制# 下载PHYLIP wget -c http://evolution.gs.washington.edu/phylip/download/phylip-3.697.tar.gz # 解包 tar zxf phylip-3.697.tar.gz # 进入程序文件夹 cd phylip-3.695/src/ # 复制文件 cp Makefile.unx Makefile # 编译 make install # 可能需要sudo 权限 conda安装代码语言:javascript复制# 新建phylip环境,并安装phylip conda create -n phylip -c bioconda phylip -y 2.2. 格式转换转换脚本下载代码语言:javascript复制# 下载 wget -c https://github.com/edgardomortiz/vcf2phylip/archive/refs/tags/v2.8.zip # 解压 unzip v2.8.zip 转换为PHYLIP matrix代码语言:javascript复制python vcf2phylip.py -i test.vcf # PHYLIP matrix是默认格式,不同输出格式,见下参数 # -f FASTA matrix # -n NEXUS matrix # -b binary NEXUS matrix注意:test.vcf中的样本名一定要少于10个字符,否则会报错 2.3. 建树构建配置文件seqboot.par代码语言:javascript复制test.phy # 本程序的输入文件 R # 选择bootstrap 100 # 设置bootstrap的值,即重复的replicate的数目,通常使用1000或者100,注意此处设定好后,后续两步的M值也为1000或者100 Y # yes确认以上设定的参数 9 # 设定随机参数,输入奇数值。 dnadist.par代码语言:javascript复制seqboot.out # 本程序的输入文件 T # 选择设定Transition/transversion的比值 2.3628 # 比值大小 M #修改M值 D # 修改M值 100 # 设定M值大小 2 # 将软件运行情况显示出来 Y # 确认以上设定的参数 neighbor.par代码语言:javascript复制dnadist.out # 本程序的输入文件 M 100 # 设定M值大小 9 # 设定随机数,输入奇数值 Y # 确认以上设定的参数 consense.par代码语言:javascript复制nei.tree #本程序的输入文件 Y #确认以上设定的参数 phylip建树代码语言:javascript复制# 在 phylip 文件夹下,依次运行下面的命令 # seqboot ./exe/seqboot < ./seqboot.par && mv ./outfile ./seqboot.out # dnadist ./exe/dnadist < ./dnadist.par && mv ./outfile ./dnadist.out # neighbor ./exe/neighbor < ./neighbor.par && mv ./outfile ./nei.out && mv ./outtree ./nei.tree # consense ./exe/consense < ./consense.par && mv ./outfile ./cons.out && mv ./outtree ./constree 3. IQ-treeIQ-tree[5]的建树方法与phylip类似,只是最后一步不一样,同样需要先转换文件格式为:phy(格式转换见2.2)。 3.1. 安装利用conda安装代码语言:javascript复制# 新建iq-tree环境 并 安装iqtree conda create -n iqtree -c bioconda iqtree -y 3.2. 建树IQ-tree 建树(简单)代码语言:javascript复制iqtree -s test.phy替代模型选择与详细的分支评估,见http://www.iqtree.org/中说明 参考资料[1] VCF2Dis: https://github.com/BGI-shenzhen/VCF2Dis [2] FastMe2.0: http://www.atgc-montpellier.fr/fastme/ [3] iTOL: https://itol.embl.de/ [4] PHYLIP 是用于推断系统发育的免费程序包。: https://evolution.genetics.washington.edu/phylip.html [5] IQ-TREE: http://www.iqtree.org/ |
【本文地址】
公司简介
联系我们