| 使用 MENA 和 Gephi 作分子生态网络分析(Molecular Ecological Network Analysis)图 | 您所在的位置:网站首页 › molecular是什么意思啊 › 使用 MENA 和 Gephi 作分子生态网络分析(Molecular Ecological Network Analysis)图 |
使用 MENA 和 Gephi 作分子生态网络分析(Molecular Ecological Network Analysis)图
|
使用 MENA 和 Gephi 作分子生态网络分析(Molecular Ecological Network Analysis)图
文章目录
使用 MENA 和 Gephi 作分子生态网络分析(Molecular Ecological Network Analysis)图简单介绍什么是MENA**什么是Gephi**
准备数据MENA网站登录和使用上传数据构建网络分析网络和导出网络文件使用Gephi作图MENA导出的数据预处理Excel打开和处理文件node文件edge文件
导入node和edge文件制图给模块标颜色给每个点按照degree设置大小设置布局和标签
简单介绍
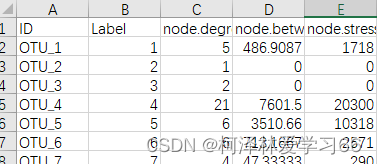
生物之间相互作用比如竞争、合作、共生等;由于进化生物之间存在某种系统发育关系,这些联系都能描述为生态网络,在生态网络中,每一个元素(生物或基因)可以描述成网络中的一个节点,他们之间的关系能描述成网络中的边。随着高通量测序、基因芯片等技术的发展,研究人员可以得到了空前庞大的数据量,而利用微生物16S测序数据得到的OTU丰度矩阵也可以进行网络分析,探究不同操作单元之间的互作关系。 什么是MENA一个可以利用OTU数据进行在线分子生态网络分析的网站。 什么是Gephi做关系网络图的软件,有可视化页面,基于Java的,不知道没装java能不能用,我之前装了而且配置过环境变量,然后Gephi打开就是能用的。 准备数据网络分析的输入数据为OTU丰度矩阵,每一行对应一个OTU,每一列对应OTU在不同样品中的丰度,如下图
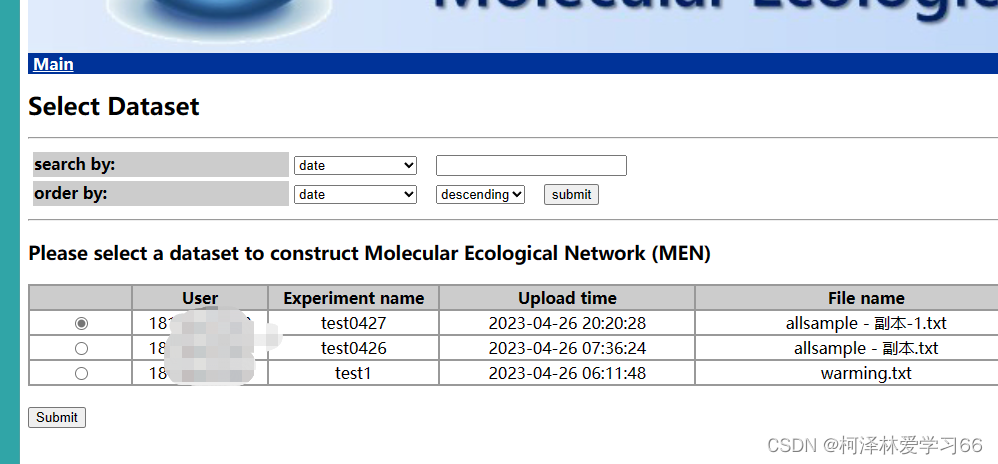
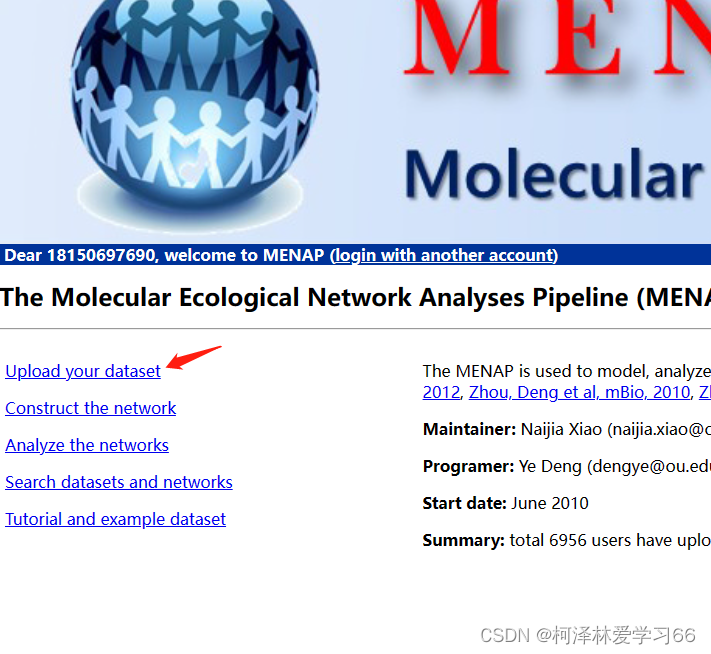
网站地址: http://ieg4.rccc.ou.edu/MENA/ 如无账号可以进行注册并登陆,注册只需要邮箱等信息即可。 登陆后界面的主要操作内容为前四部份,涉及上传数据、构建网络、分析网络以及查看此前上传和分析的网络结果。 点击 选择文件 然后点击提交 提交成功后会自动显示上传数据的大致信息,包括样本数量、OTU数量等等。 构建网络点击
选择你需要分析的数据集,提交
跳转到Select Dataset页面,选择需要进行网络分析的数据进行下一步,提交之后进入参数设置页面(如下图),具体涉及了数据过滤,相似性计算算法,RMT(随机矩阵理论)模型计算,提交后跳转至等待页面。
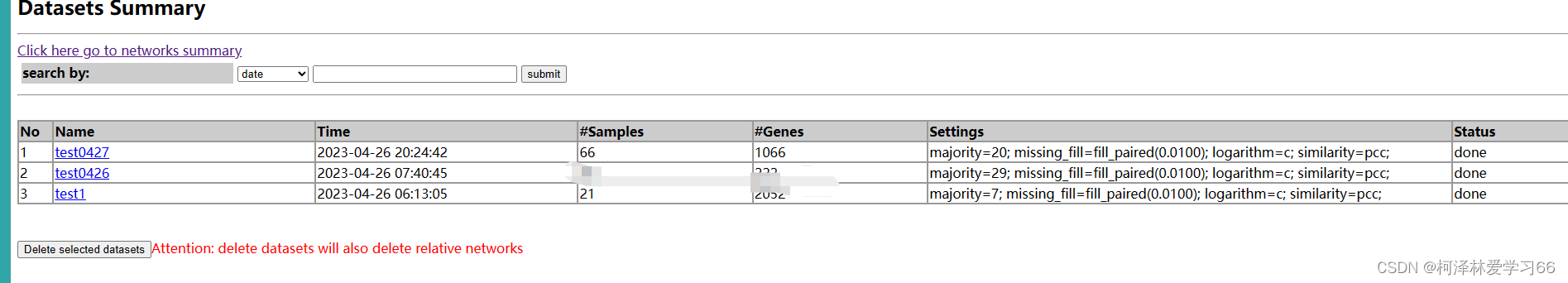
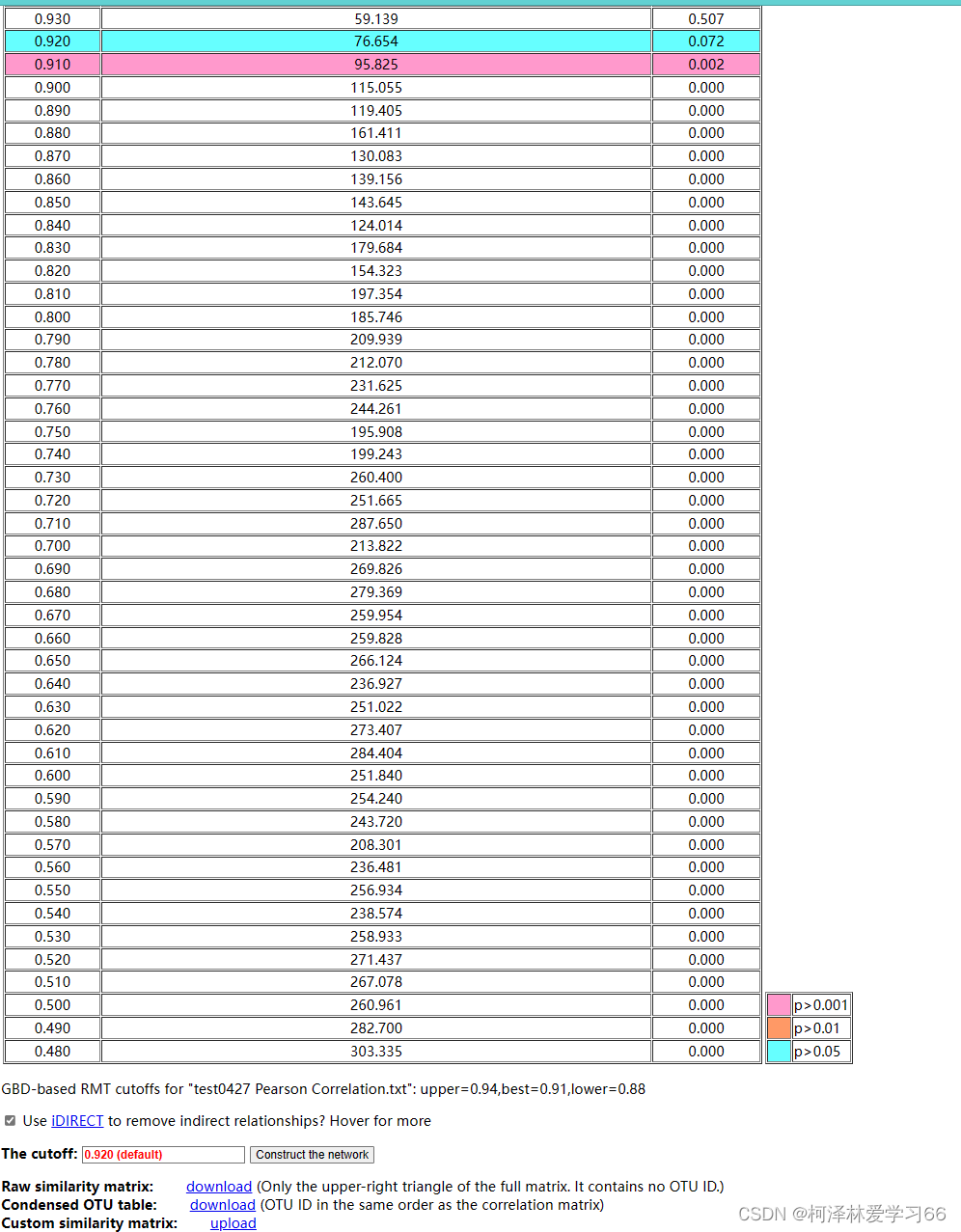
主界面点击“Search datasets and networks”,可查看当前的工作状态,Status显示为“done”时就可以了。(此步耗时可能比较长) 点击对应结果 选择一个合适的cutoff作为相似矩阵来构建网络 通常而言,cutoff选择的阈值越高,网络规模(节点数和边数)越小,拟合的R2也高。 多个网络需要比较,保持在同一(或尽可能接近的)cutoff值
点击提交。随后,将显示最终网络的节点数、边数、平均连通度、平均路径长度、拟合的R2。 返回主界面点击“Analyze the networks”,可对网络执行以下操作。
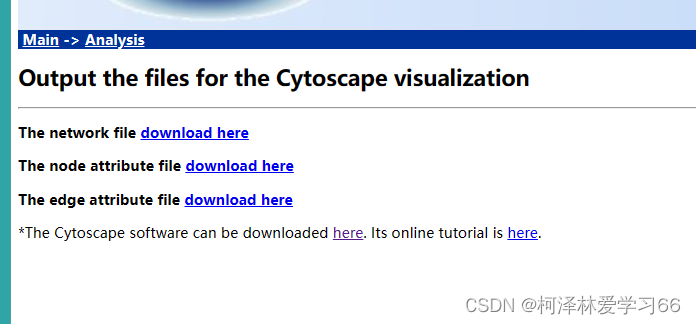
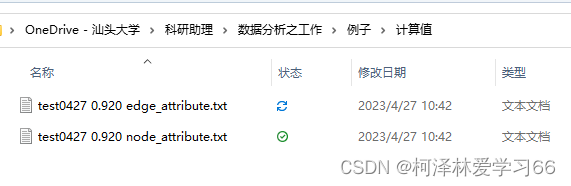
做完模块计算后。可以点击导出网络文件,下载边文件和节点数据。这在后面的作图中需要。
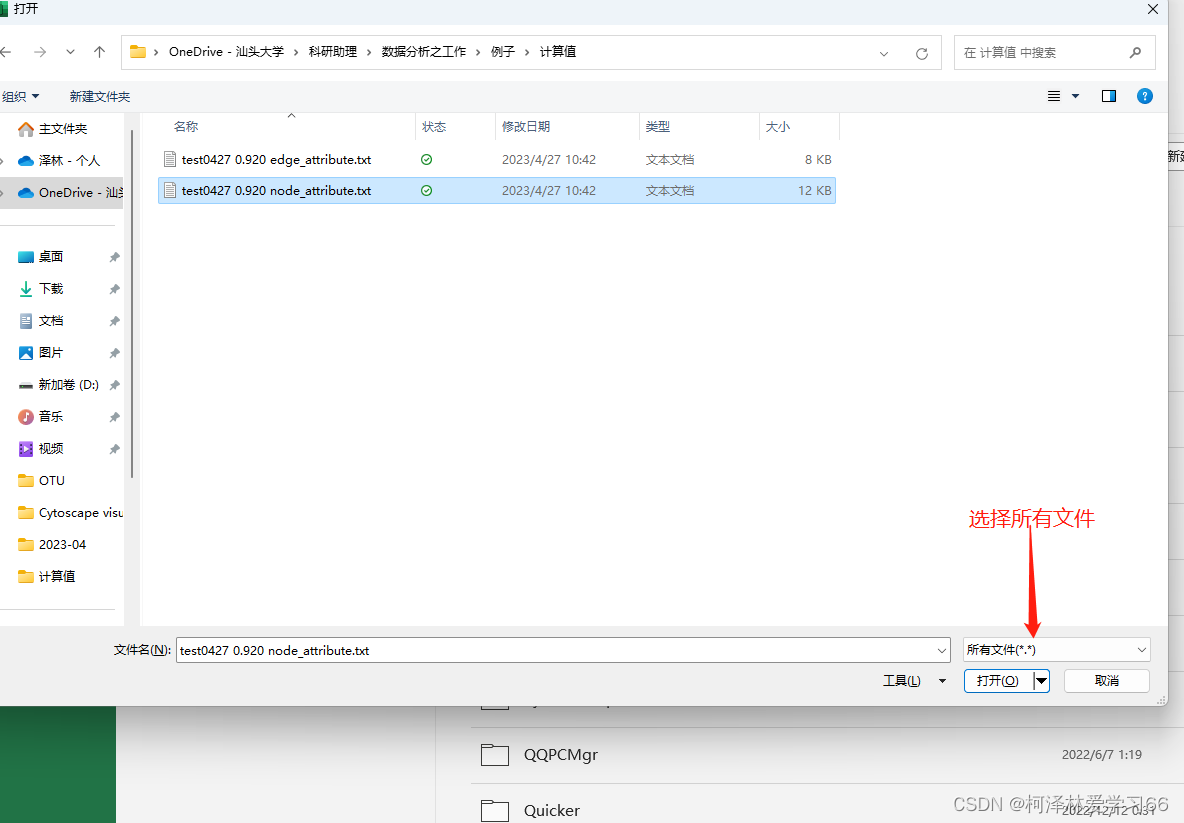
作图的原理是:边文件(edge)给节点之间相连的信息,节点文件(node)补充节点的细节信息,比如rank等。所以边文件是必须的,实际上没有节点文件也能把图做出来,软件也支持导入邻接矩阵文件作图。 MENA导出的数据预处理因为MENA导出的数据是以分隔符保存的文件,如果用Gephi打开标签不全没法打开,edge文件更是没有属性标签。所以用之前必须先加上,并且另存为Gephi能识别的.lsx文件。这些步骤使用excel就能完成 Excel打开和处理文件
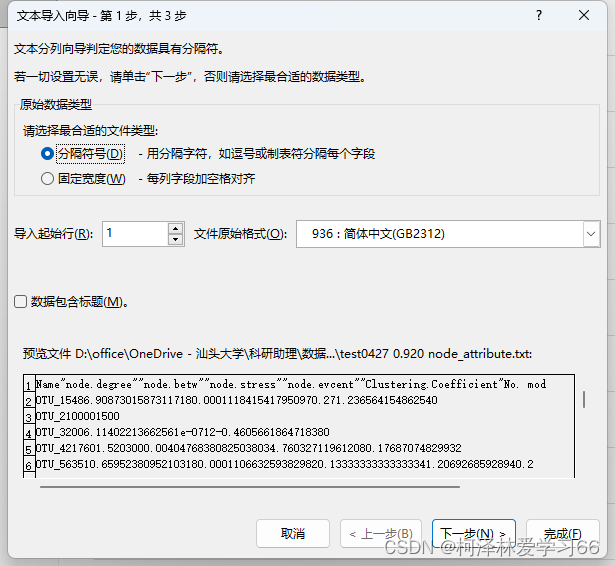
选择分隔符
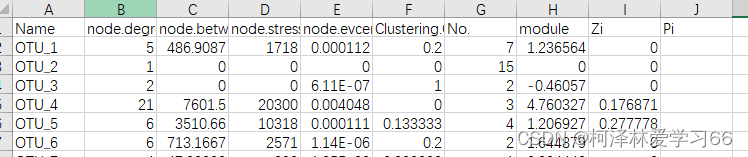
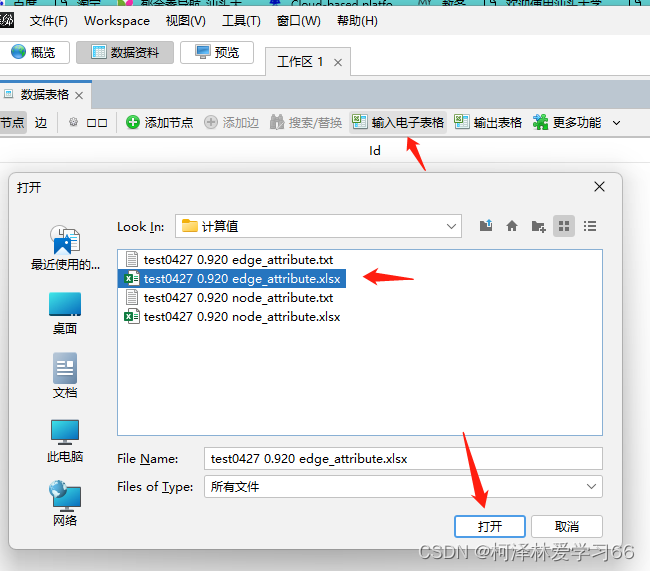
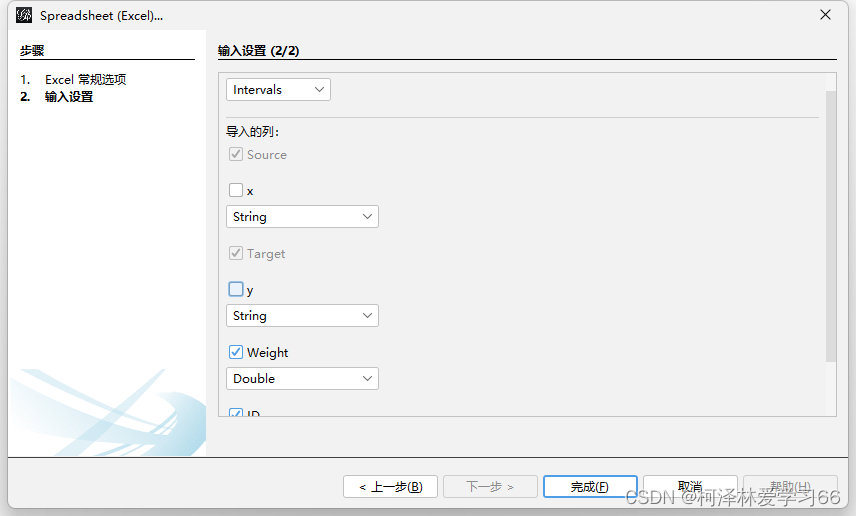
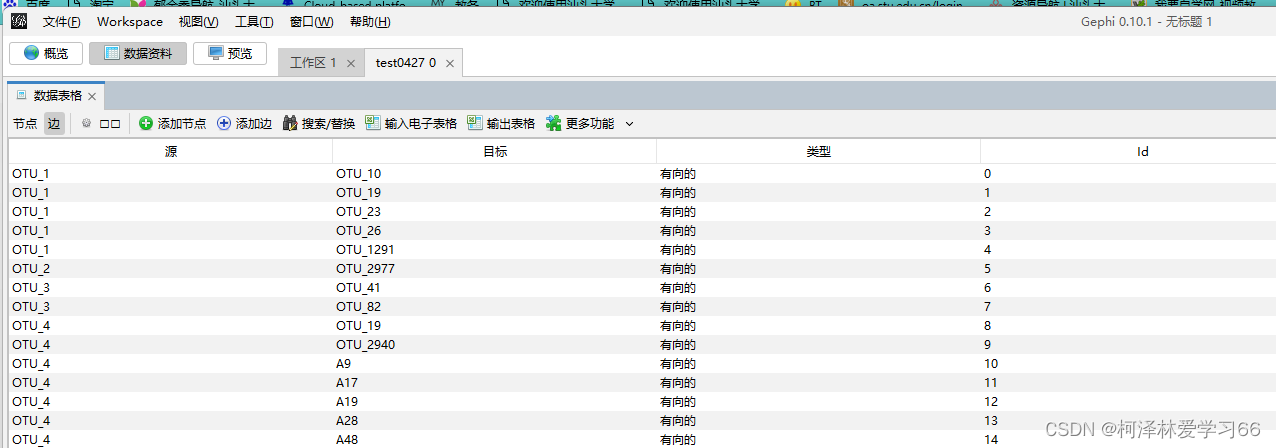
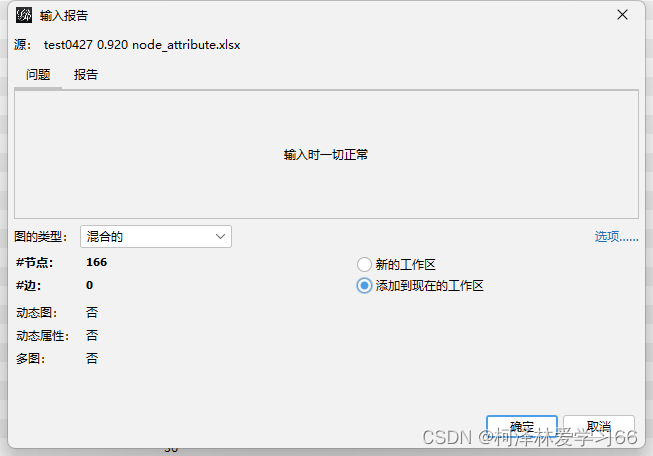
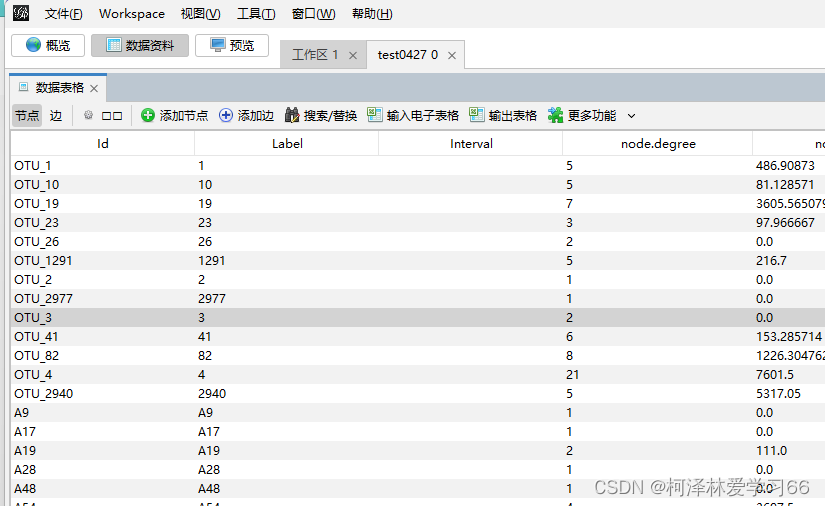
点下一步,选择空格分隔符,完成 node节点文件需要补充的属性标签是: 1:ID,(为了和边文件匹配) 2:Label,(作图的时候显示) 我的做法是,把Name复制一列,然后第一列改成ID,第二列改成Label,然后把数据中的无关符号去掉,保留数字。(具体处理方式依照作图需求,这边依照的是老师给的格式,多组处理使用R或python会方便很多) 结果: 另存为xlsx文件 edge文件node节点文件需要补充的属性标签是: SourceTargetWeightIDType实际上会发现用同样方法打开edge文件后格式是这样子: OTU_1(pp)OTU_10=1OTU_1(pp)OTU_19=1OTU_1(pp)OTU_23=1OTU_1(pp)OTU_26=1OTU_1(pp)OTU_1291=1OTU_2(pp)OTU_2977=1OTU_3(pp)OTU_41=1其中。第一列和第三列和第5列是我们要用的值 分别的意义为:源节点,终结点,和权重 此外,我们还需要加入ID和type(是否有向边) 加上标签后: SourcexTargetyWeightIDTypeOTU_1(pp)OTU_10=10DirectedOTU_1(pp)OTU_19=11DirectedOTU_1(pp)OTU_23=12DirectedOTU_1(pp)OTU_26=13DirectedOTU_1(pp)OTU_1291=14Directedx和y是随意取的,因为文件是以空格为分隔符的,不能空着。 保存为.xlsx文件 导入node和edge文件打开Gephi软件 导入边文件: 点下一步,没用的值就不用勾选了 点击完成 点击“边”查看: 再同样导入node文件 注意要加入现有的workspace 可以看到节点现在有详细数据了
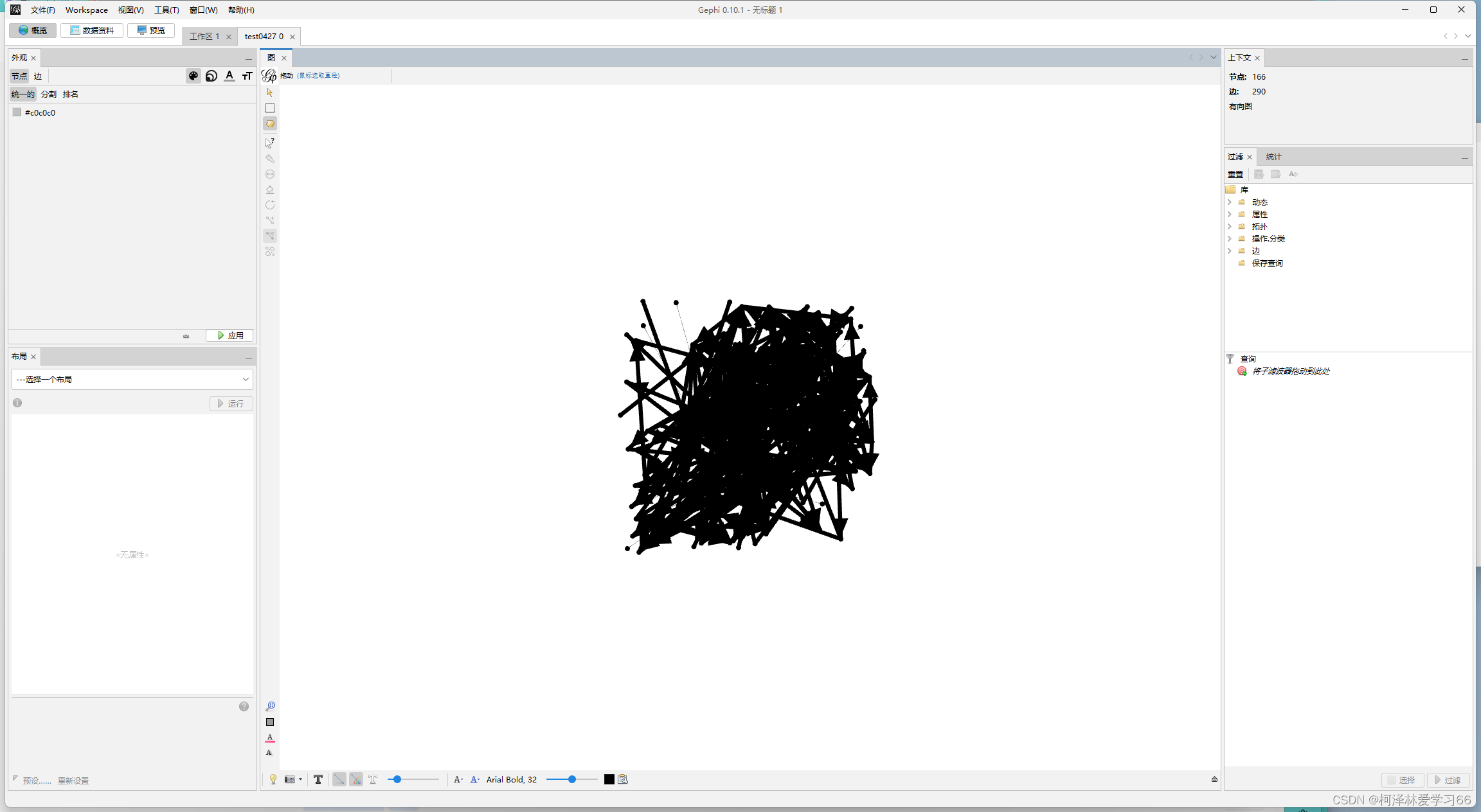
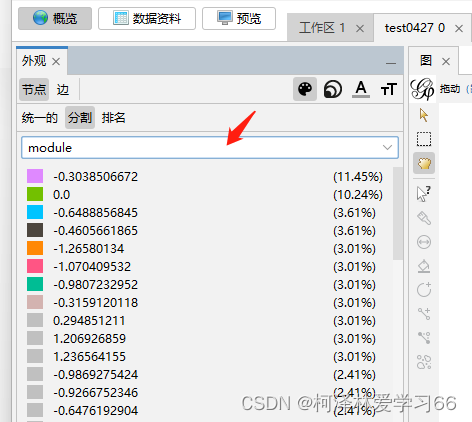
点击预览(overview): 拖动左下角使变清晰 因为node文件里面有了MENA分析后的注释信息,包含mudule、degree等,我们下一步的目的就是将这些注释在图上体现出来
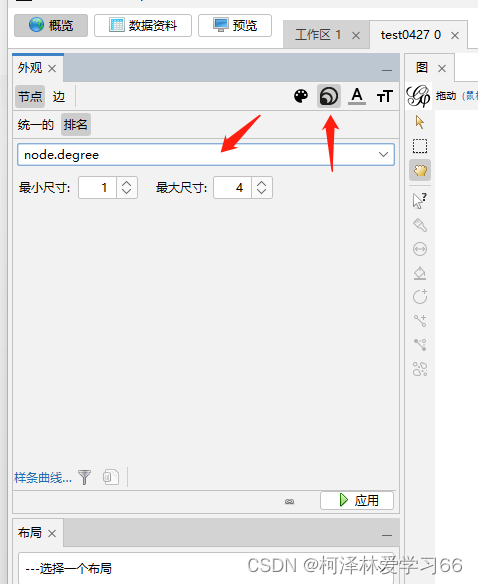
设置颜色 点击apply
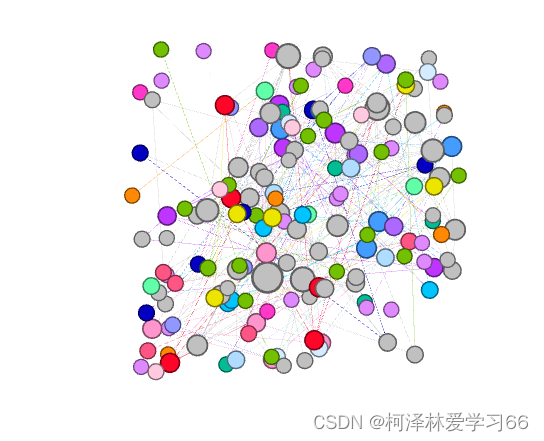
我设的是min25,max50: apply: 布局选择Fruchterman Reingold run后
概览点击刷新:
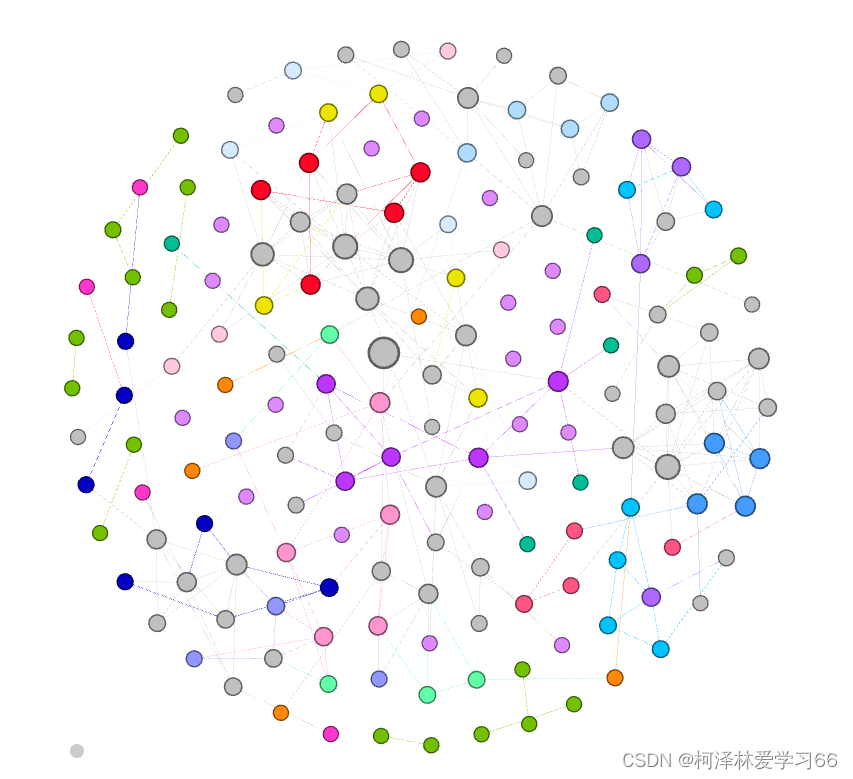
给图加上节点标签:
点击刷新:
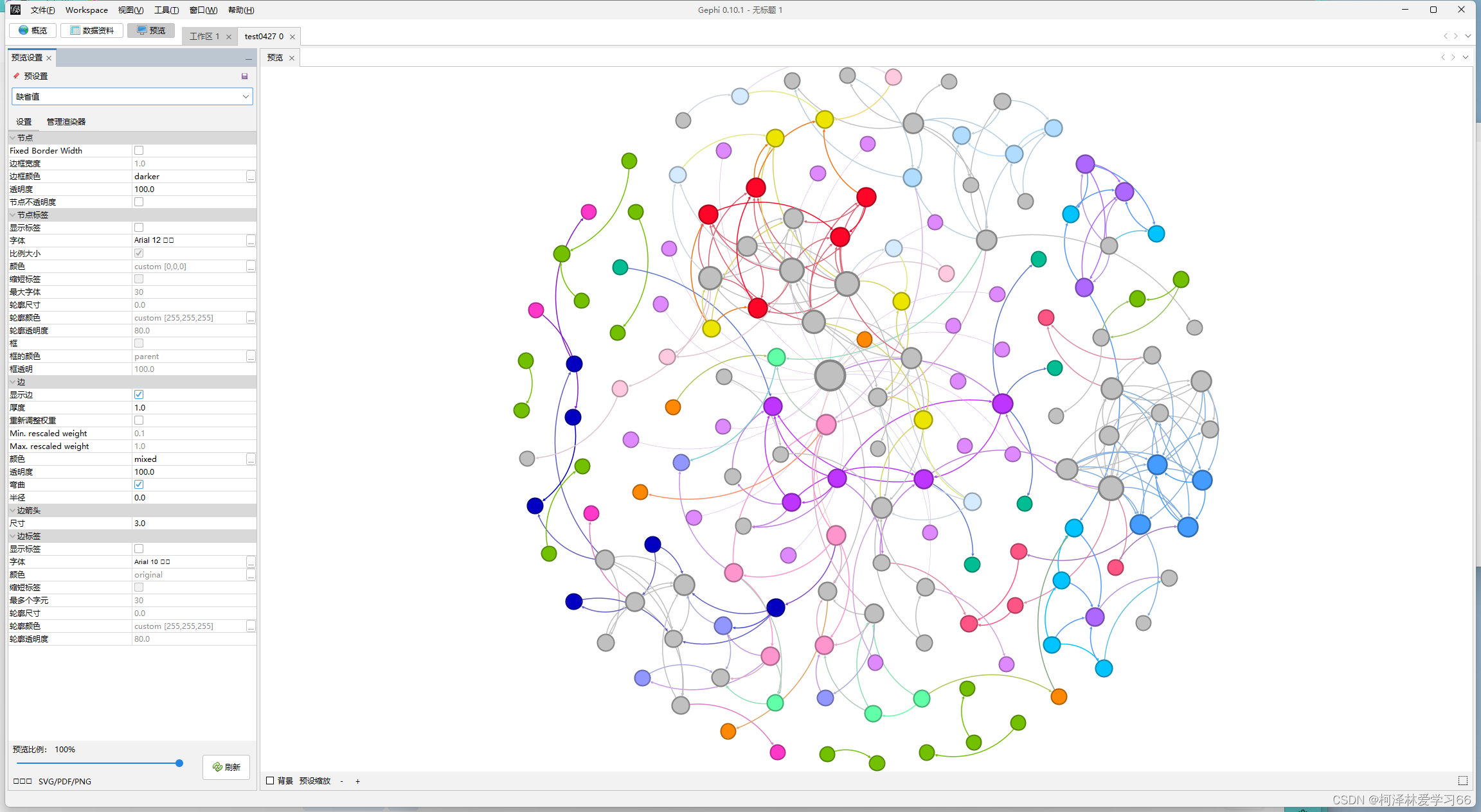
最后就可以保存和导出了 由于在计算时过滤条件放宽了,导致节点较为分散 ········································································ 部分内容参考至CSDN博主「weixin_39532019」的原创文章, 原文链接:https://blog.csdn.net/weixin_39532019/article/details/111686206 |
【本文地址】
![[外链图片转存失败,源站可能有防盗链机制,建议将图片保存下来直接上传(img-584heqFU-1682576580008)(C:\Users\24121\AppData\Roaming\Typora\typora-user-images\image-20230427091644079.png)]](https://img-blog.csdnimg.cn/5ea0aee501214b6186a0b8fe88ca9fea.png)


![[外链图片转存失败,源站可能有防盗链机制,建议将图片保存下来直接上传(img-ViAEvGvw-1682576580010)(C:\Users\24121\AppData\Roaming\Typora\typora-user-images\image-20230427092404089.png)]](https://img-blog.csdnimg.cn/f601c33b247d4ba3bd61e15841cf713e.png)